产品优势
保证质量的同时大大缩短周期
一次性获得真菌近完成图
大幅度提升组装指
方案策略
| 测序平台 | 测序策略 | 参考指标 | 交付周期 |
| Nanopore PromethION | 1D文库 ≥100×测序深度 | Contig N50>1Mb Contig Number<3N 单碱基错误率:<0.01% 基因组覆盖度:>98% 基因区覆盖度:>99% | 建库测序:12个工作日 标准分析:15个工作日 高级分析:根据实际的信息 分析内容而定 |
| PacBio Sequel | 20kb SMRTbell文库 CLR测序 ≥100×测序深度 | Contig N50>1Mb Contig Number<3N 单碱基错误率:<0.01% 基因组覆盖度:>98% 基因区覆盖度:>99% | 建库测序:18个工作日 标准分析:15个工作日 高级分析:根据实际的信息分析内容而定 |
备注:组装指标基于单倍体基因组样本而定。对于以下较复杂的情况不能在上述策略中保证近完成图,或需要修改方案:
- 基因组大小>60Mb,
- 样本不纯,
- 基因组杂合度>0.5%,
- 重复序列比例异常高(>15%)。
分析内容
标准分析
- 数据质控
- 基因组组装
- 基因组结构预测
- 基因功能注释
高级分析
- 基因家族分析
- 系统发育分析
- 共线性分析
- 基因组大片段复制
- PHI数据库注释
- CAZy数据库注释
- 次级代谢产物分析
个性化分析
根据客户需求提供定制化服务
结果展示
1.基因组组装及评估
质控过后,利用过滤后的reads进行纯三代组装,通过NextDenovo软件对基因组进行组装,并进行BUSCO评估、CEGMA评估、序列一致性评估和GC-Depth分析。
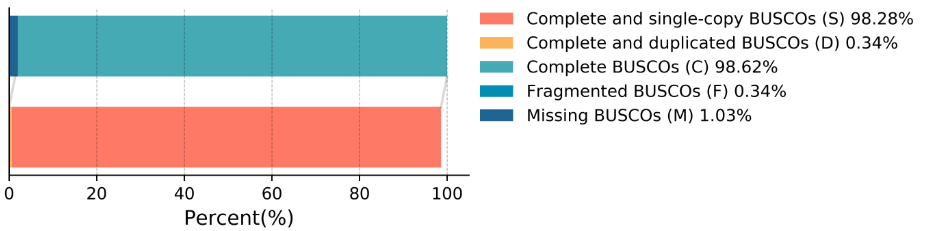
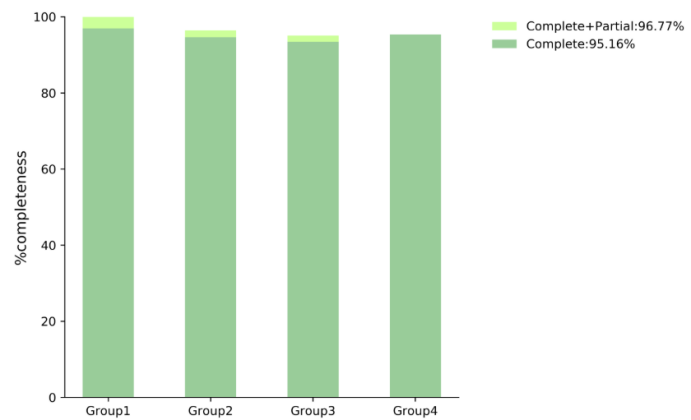
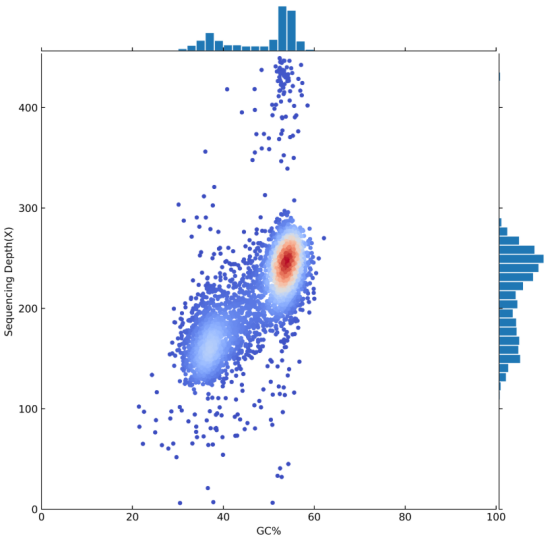
BUSCO评估、CEGMA评估和GC-Depth分析展示
2.基因组注释
对组装的基因组进行结构和功能注释并对注释结果进行评估。
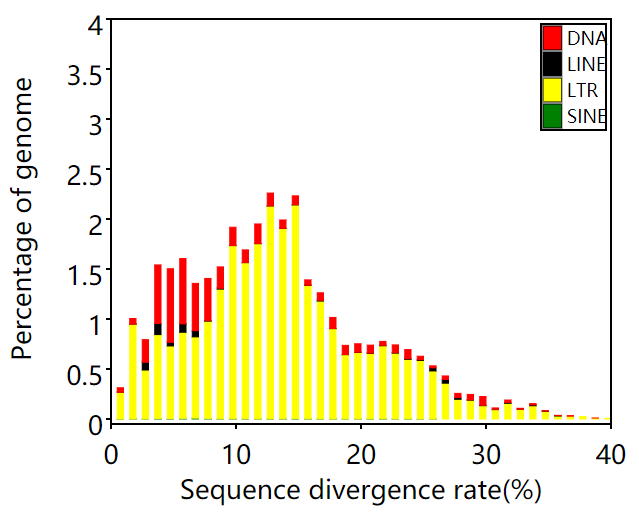 转座子分化率
转座子分化率
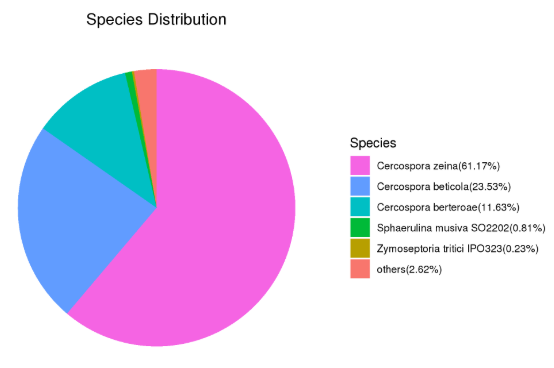 NR库注释结果对应物种分类图
NR库注释结果对应物种分类图
 各数据库注释结果韦恩图
各数据库注释结果韦恩图
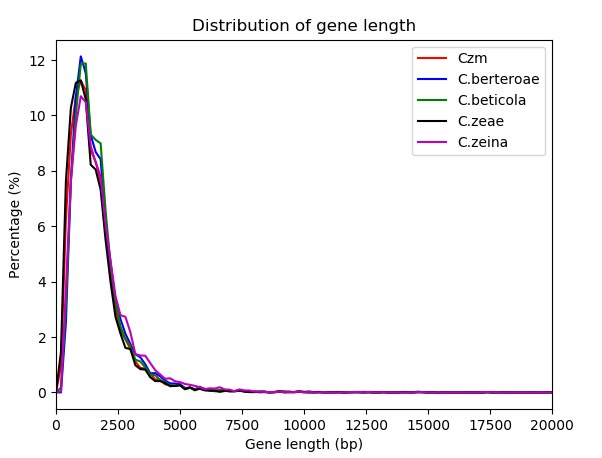
其它近缘物种基因各元件分布图
常见问题
1. 对于共生真菌是否可以进行基因组测序?
如果与真菌共生的物种基因组已知,可以通过基因组比对过滤的方式获得真菌序列进行组装。
2.关注的某个基因在结果中没有找到是什么原因造成的?
由于真菌全基因组数据库相对来说较少,有可能是在注释的数据库中还没有该基因的信息,所以无法注释出来;另一方面,基因组注释都是预测的结果,也有可能该株菌中不存在这个基因,需要通过其它方法进一步确认。
案例解析
案例分析
案例解析
酵母基因组de novo组装及群体遗传变异研究
在长读长测序技术中,Nanopore由于其快速、低成本以及便于使用的优点,越来越受到研究者的青睐。本研究即利用Nanopore得到Saccharomyces cerevisiae S288C菌株的基因组近完成图,获得转座子元件和端粒区域。
该研究选取或不同地域来源,或具有不同生态学功能,或在1002酵母基因组项目中显示有较大遗传变异的酵母菌21株,以及S288C菌株进行Nanopore长读长测序,并利用Illumina reads进行校正,组装得到的基因组结果如表1所示。基因组大小介于11.83Mb到12.2Mb之间。菌株CEI的Contig数最少(18),BAMI的Contig数最多(105),平均contig数为27.5,组装结果都较完整。
为了获得21株酵母菌的转座子全局视图,研究者利用组装得到的高质量基因组绘制了21株酵母菌的转座子图谱(Fig.1)。将组装得到的基因组与已知的酵母TE家族(Ty1-Ty5)进行比对,发现S288C组装注释的50个 TEs有47个都在染色体的正确位点,只有3个Ty1位点未被鉴定,表明Nanopore策略组装的基因组用于鉴定TE准确性较高。
正是由于Nanopore组装基因组的高完整性,我们能够获得在短读长测序中被遗失的信息,如转座子元件插入以及结构变异等。同时,该研究表明Oxford Nanopore技术可用于de novo测序和组装,但是由于其碱基的随机错误,仍需要二代数据进行polishing。
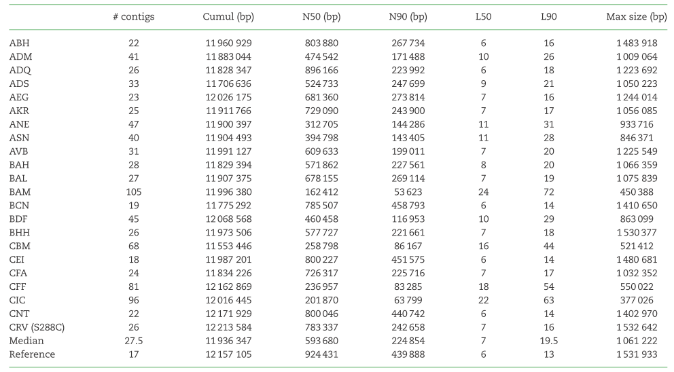 图1:Table 1 22株酵母基因组组装结果
图1:Table 1 22株酵母基因组组装结果
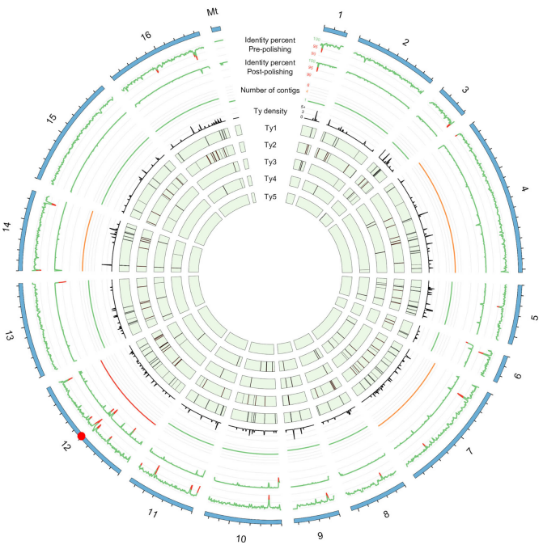 图2:酵母Ty转座子家族图谱
图2:酵母Ty转座子家族图谱
参考文献:
Istace B, Friedrich A, d’Agata L, et al. de novo assembly and population genomic survey of natural yeast isolates with the Oxford Nanopore MinION sequencer [J]. Gigascience, 2017, 6(2): 1-13.



