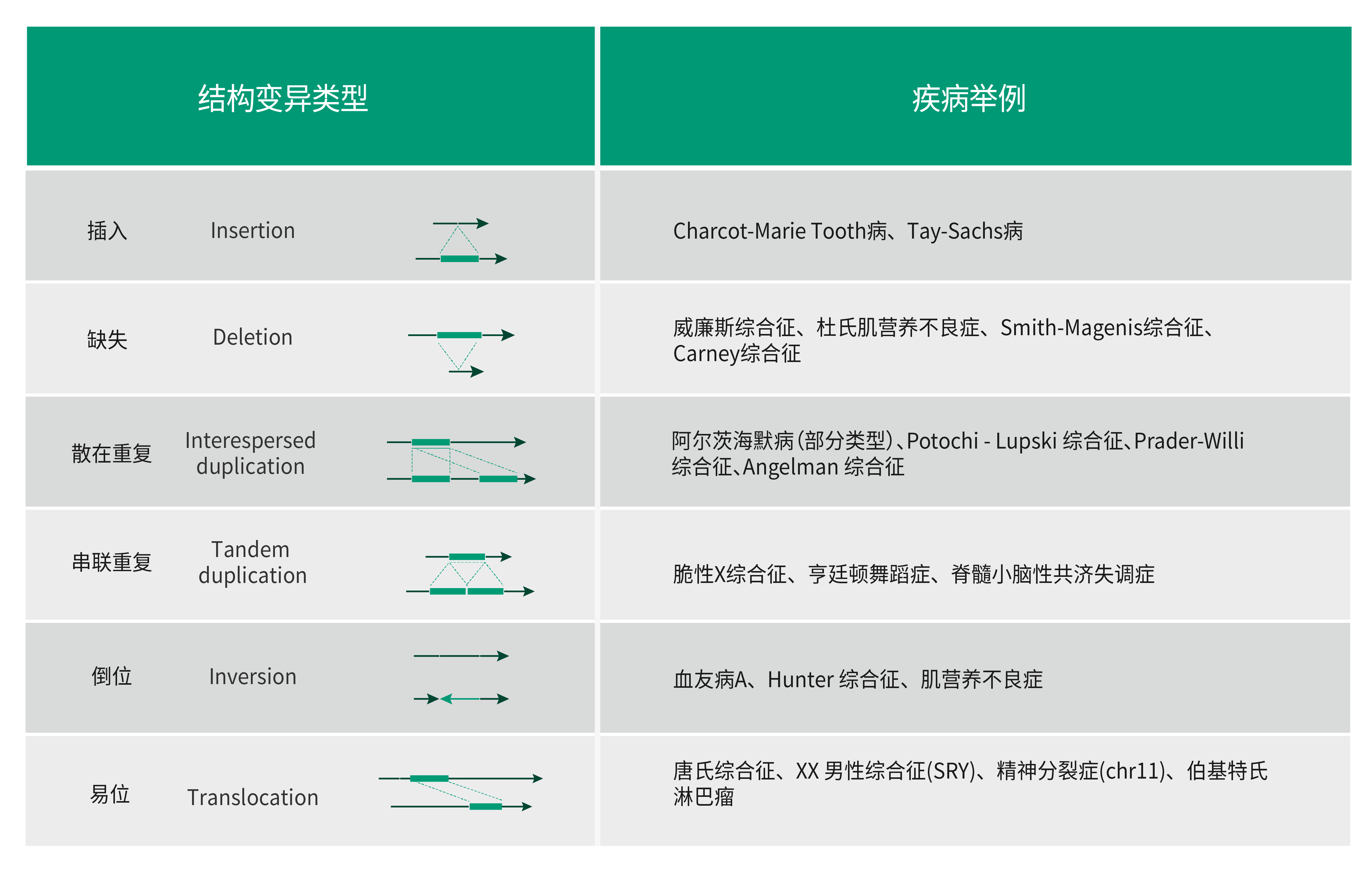
结构变异与疾病
基因变异是导致人类遗传病的重要原因,约80%的临床罕见病被认为是由遗传因素所导致。致病变异从大小来说,可分为单个碱基对的变异(SNVs)、小的插入或缺失(InDels≤50bp)以及结构变异(SVs>50bp)。
结构变异包括DNA序列的插入、缺失、重复、倒位、易位等,影响基因组的稳定性、相关基因的表达调控,进而决定物种表型。据统计,每个人类基因组都有超过20000个结构变异,基因组结构变异可能导致的疾病已经超过1000种,其中不乏我们常常耳闻的渐冻症、精神分裂症以及癌症。这些变异带来的影响比SNVs或者是InDels带来的影响更大。
短读长测序,对SVs的检测无能为力
近年来全外显子组检测(WES)已成为孟德尔遗传病的主流临床研究或检测方法,然而,由于二代测序技术的读长较短,WES的大部分检测结果(约60-70%)为阴性。即使基于二代测序的全基因组测序(Whole-genome sequencing, WGS)似乎也不能显著提高诊断率,且性价比不高。因此,WES / WGS阴性病例已成为目前遗传病临床研究或诊断的巨大挑战,其中最主要的原因是,基于二代测序技术的WES和WGS对结构变异等复杂区域的检测常常无能为力。
长读长测序技术,也被称为第三代测序技术,凭借长读长、无PCR过程、可轻松跨越基因组重复区域、高GC区域等优势,弥补了传统测序技术对结构变异的漏检,为揭秘更多的“基因组暗物质”提供了更有力的支持,从而提高更多疾病的诊断率。
希望组基于Oxford Nanopore、Bionano等测序技术,并配合自主研发的基因组结构变异自动化分析工具NextSV,可以很好的检测复杂的结构变异,极大的提高了SVs的检出率和准确度,目前已重磅推出“华夏万人SV”项目。
华夏万人SV
“华夏万人SV”是继“华夏一号”和“中华家系一号”后的又一重大计划,将对不少于10万个中国人个体进行全基因组三代测序,旨在构建中国人群高分辨基因组结构变异图谱、单碱基精确度的DNA甲基化图谱,弥补目前基因组数据库的空白,进而通过对大规模的疾病群体进行基因组结构变异分析,明确广泛的疾病和病症相关的罕见遗传变异。“华夏万人SV”将对中国人群基因组学研究、遗传性疾病研究、精准医疗应用等领域产生重要的科学及临床价值。
技术路线