技术突破丨希望组“10X+ONT-Q20+”长读长单细胞测序实测通过!!!
2021年ONT在科研团体大会(Nanopore Community Meeting)上发布了”Q20+”试剂产品。这是利用包含最新“Q20+”化学试剂并支持“双链”(Duplex)测序的新试剂盒LSK112和最新芯片R10.4相结合的测序技术,可以实现>99%的原始reads(单链)准确度,或约Q30的双链(Duplex)准确度。
希望组(GrandOmics)作为中国最早开展ONT测序服务的公司之一,一直走在技术应用的前沿,率先将高通量单细胞分选平台10X和ONT最新技术进行组合创新,给火热的单细胞测序领域,提供了全新的技术解决方案。
测试背景
2020年8月于Nature Communication杂志发表的题为“High throughput, error corrected Nanopore single cell transcriptome sequencing”的研究论文,将单细胞与Nanopore全长转录组进行了技术整合,使得在单细胞水平上检测差异RNA剪接和RNA编辑成为可能。利用Illumina对10X Genomics文库进行短读长测序,为每个基因和基因组区域定义相关的Cell Barcode,随后为每个细胞、基因或基因组区域定义相关的UMIs组合。进而利用上述信息指导Cell Barcode和UMI分配到已比对至基因组上的Nanopore reads,通过对相同UMI的reads进行分组,校正和拆分Nanopore测序reads,用于开展下游的isform分析和RNA编辑。考虑到ONT-Q20+测序即将成为行业新的长读长测序技术标准,我们迫不及待的进行了新的尝试。
测试方式
10X单细胞平台获得的全长cDNA分成两份,一份进行常规二代测序,另外一份进ONT Q20+R10.4测序,利用二代测序数据的UMI指导进行 ONT测序的数据拆分。
测试样本
某人类PBMC样本,采用最新GPU进行Super高精准度Basecalling。尽管大大提高了计算消耗,但预期可以得到最佳的单碱基质量。
测试结果
一、下机数据统计
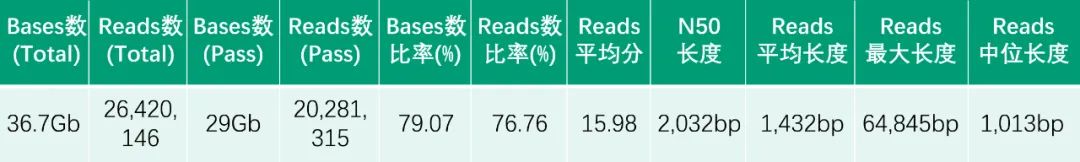
下机数据质控统计表
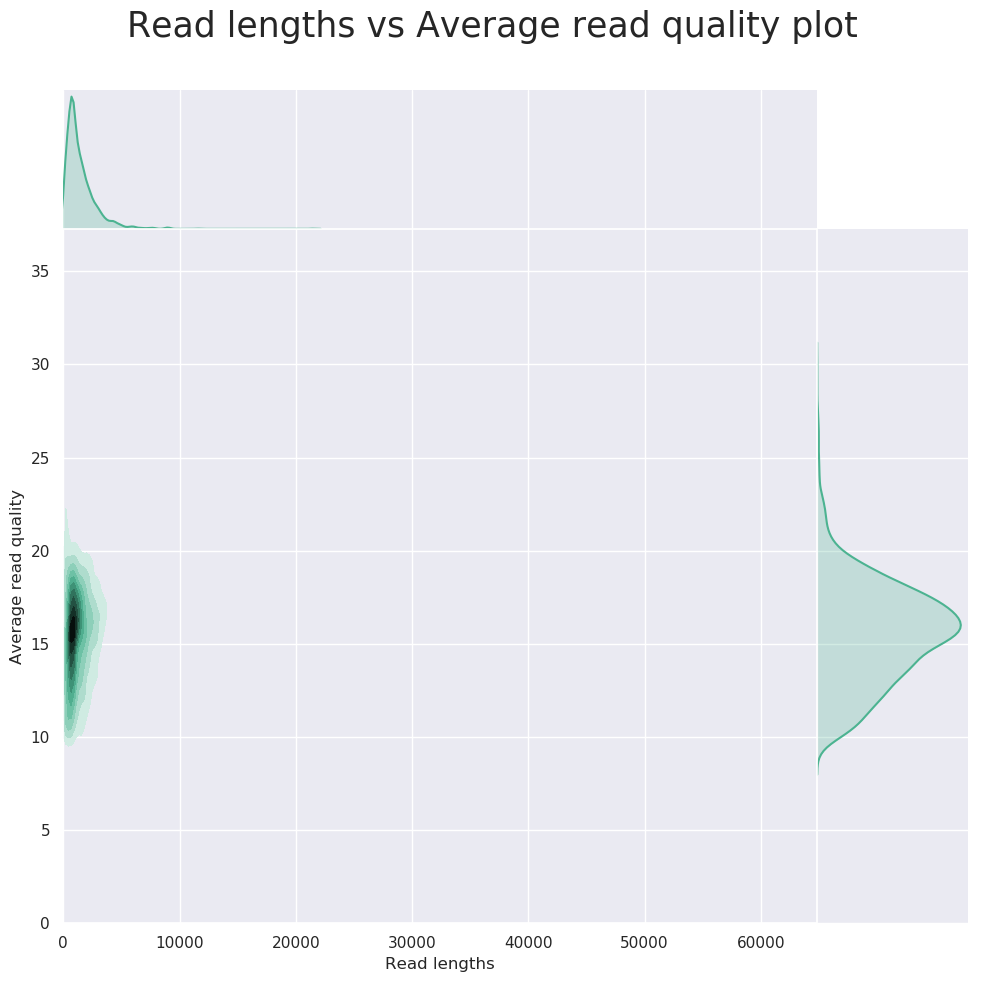
Reads长度分布图
单张测序芯片的产量为36.7Gb,pass产量为29Gb。尽管产量仍有提升空间,但通过芯片及算法的升级,basecalling的准确度有了大幅度的提升,reads平均分可达到15.98,最终获得了20 Mb的reads进行下游分析,和其他长读长平台所产生的reads数相比,有着明显的产量优势。该芯片样本为单链测序样本,相信在”Duplex”的模式下,样本的测序准确度会有更进一步的提升。
2. 与参考基因组比对identity
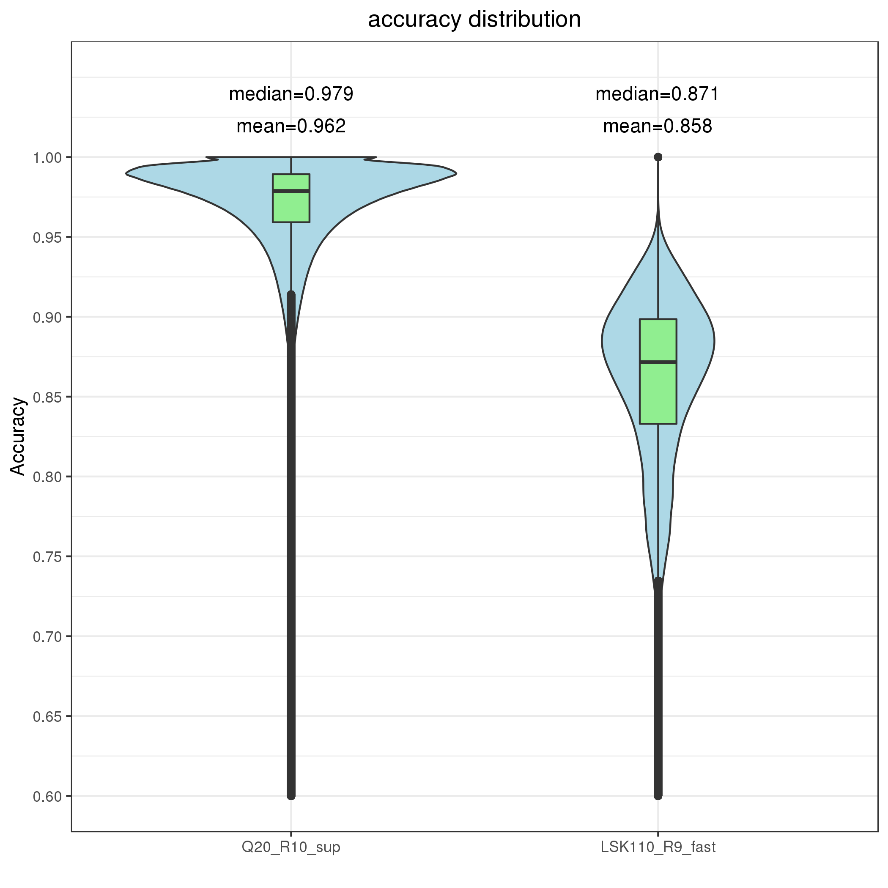
左图Q20+R10.4的比对identity分布图,右图为LSK110 R9芯片的比对identity分布图
从图中可以发现,同个样本不同的测序试剂和芯片,对于最终比对identity的准确性有着显著的差异。LSK110 R9 base-calling fast模式的比对identity中位值在87.1%,Q20+R10.4的比对identity中位值达到了97.9%。整体数据的准确度有了明显的提升。
3.数据分解率
随着数据准确性的不断提高,利用二代UMI数据指导拆分三代全长转录组数据的比例也会有相应的提升空间,内部数据表明二代UMI数据指导拆分三代全长转录组数据的拆分率可达70%,远远高于Nature Communication文章里50%的拆分率。相信在“Duplex”模式下的数据表现会有更加亮眼。敬请关注希望组后续的相关报道!
当10x单细胞样本遇上Oxford Nanopore Q20试剂及R10.4芯片,有效提升UMI的数据拆分率,拥有更多有效数据进行下游分析。尽管“Q20+”目前处于试测阶段,但相信未来在基因组、转录组上的应用场景会不断增加。希望组早在2020年年底已经推出了利用纳米孔平台进行单细胞全长转录组的产品SCAN-seq。现在有了Q20试剂的加持,拓宽了单细胞全长转录组的应用场景和需求,可以为广大科研工作者提供更好、更优质、更前沿的技术!




发表评论
想参加讨论吗?请尽情讨论吧!