产品优势
泛基因组运用高通量测序及生物信息分析手段,通过具有内在关联的不同亚种个体测序分析,并分别进行组装,不仅可以获得多个基因组信息,完善该物种的基因集,还可以获得个体特有的DNA序列和功能基因信息,有利于理解物种形成的分子进化机制及其与自然选择的关系。
方案策略
| 物种类型 | 简单基因组 | 复杂基因组 |
| 定义 | 基因组大小<2Gb 杂合度<0.5% 重复序列比例<50% | 基因组大小>2Gb 杂合度>0.5% 重复序列比例>50% |
| 文库类型 | Nanopore Ligation 1D文库 Nanopore Ultra-long reads 文库 PacBio CLR文库 PacBio HiFi reads文库 | |
| 测序策略 | 一个精细图谱推荐策略:100X Nanopore/PacBio CLR+50X NGS;更高组装指标可结合Nanopore Ultra-long reads,PacBio HiFi reads,以及Bionano和HiC技术 其它草图推荐策略:50X Nanopore/PacBio CLR | 视具体物种而定 |
| 精细图谱承诺指标 | Contig N50>1Mb | 视具体物种而定 |
分析内容
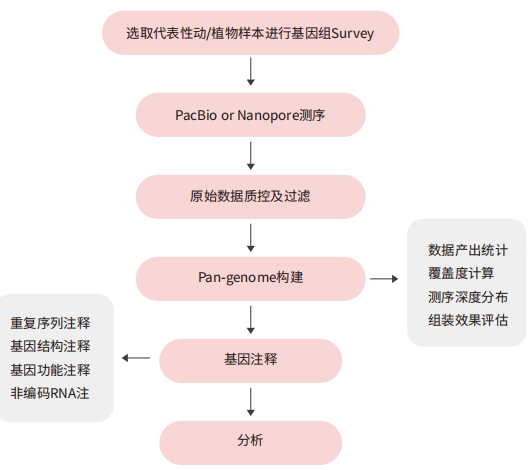
案例解析
案例分析一
案例解析
案例一 Nature Genetics‖725个番茄泛基因组揭示番茄驯化过程基因变化
本研究基于725个代表性番茄种质的基因组序列,使用’map-to-pan’策略构建了番茄泛基因组,捕获了4,873个参考基因组 中不存在的蛋白质编码基因,揭示了在选择下重要功能基因不同程度的存在/缺失变异(PAV),鉴定了一个启动子变化导致的稀有等位基因TomLoxC,并分析了其在驯化过程中的变化。泛基因组增加了番茄参考基因组的深度和完整性,对未来的生物发现和育种具有重要意义。
泛基因组包含351Mb序列,包括372个SLL(S. lycopersicum var. lycopersicum),267 个SLC(S. lycopersicum var. cerasiforme),为栽培番茄;以及78个SP(Solanum pimpinellifolium)和8个SCG(S. cheesmaniae and S. galapagense)为野生番茄,观察到25.8%的基因表现出不同程度的PAV,表明至少部分遗传多样性减少可归因于驯化和改善过程中的亚基因损失。
针对影响下游基因表达的启动子区域的选择也形成了番茄驯化和遗传结果的改善。TomLoxC启动子的非参考等位基因在驯化期间的强烈负选择,这表明由于现代番茄育种主要集中在产量、保鲜期、对生物和非生物胁迫的抗性等性状,往往忽略了难以选择的感官/香气质量特性,导致与风味相关的挥发物的减少。
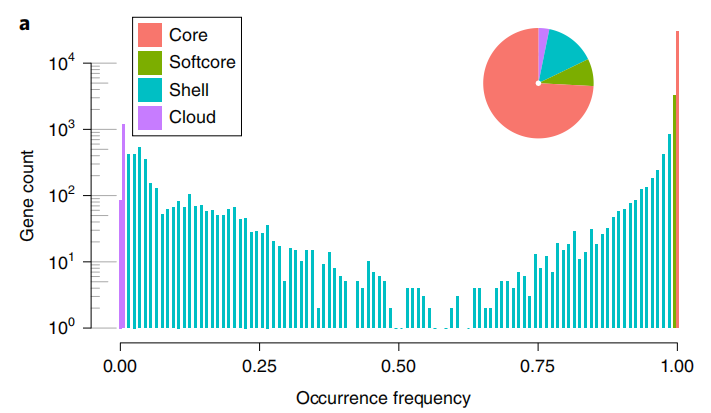
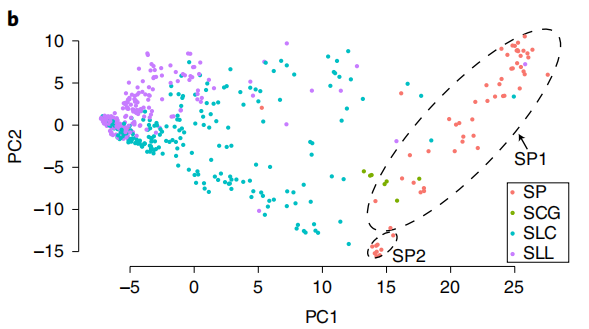
图1 番茄泛基因组组成及PAV主成分分析
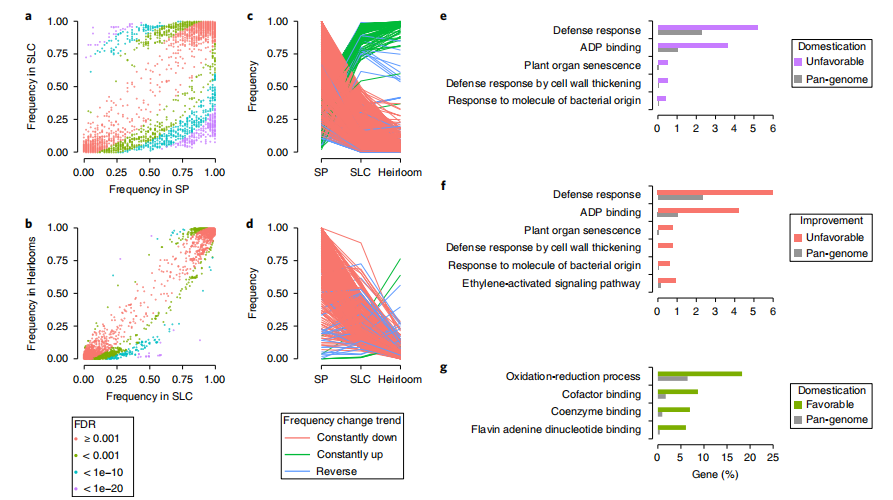
图2 番茄驯化改良过程中的基因选择偏好



