方案策略
| 测序平台 | 测序策略 | 参考指标 | 交付周期 |
| Nanopore PromethION | 1D文库 ≥100×测序深度 | 完成图 单碱基错误率<0.01% | 建库测序:10个工作日 标准分析:6个工作日 高级分析:根据实际信息分析内容而定 |
| PacBio Sequel | 10kb SMRTbell 文库 ≥100×测序深度 | 完成图 单碱基错误率<0.01% | 建库测序:16个工作日 标准分析:6个工作日 高级分析:根据实际信息分析内容而定 |
备注:线粒体/叶绿体基因组测序中,需提供线粒体/叶绿体基因组含量在10%以上的总DNA样本。
分析内容
1、数据产出以及数据质控
2、完成图组装及组装结果评价
3、基因组注释
4、基因组圈图
结果展示
基因组结构注释
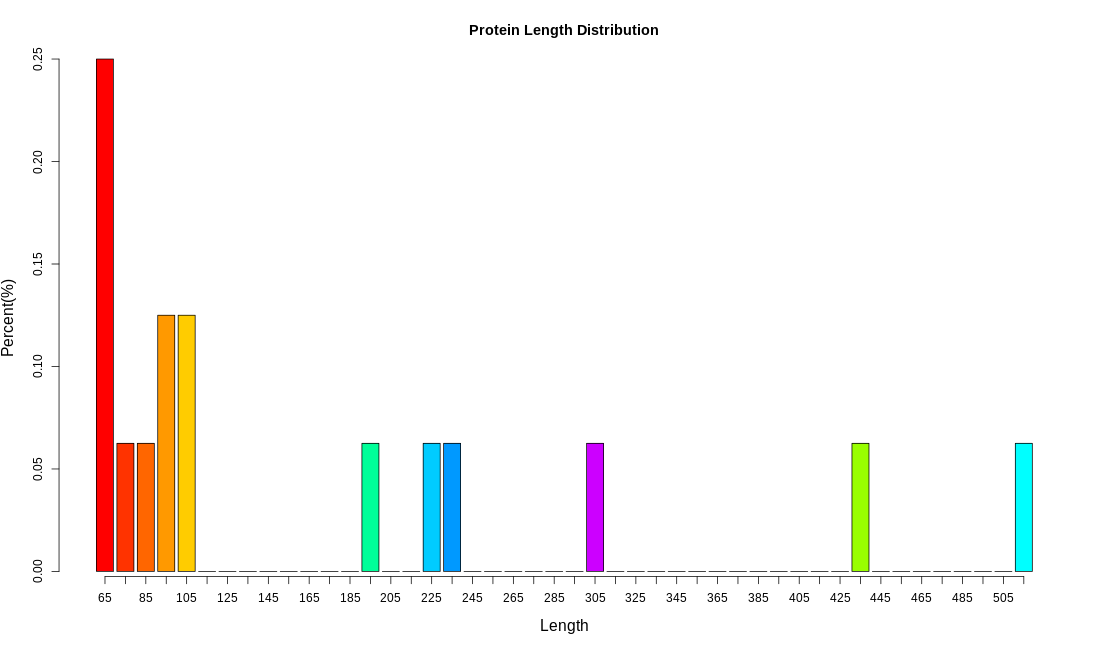 编码蛋白长度分布
编码蛋白长度分布
基因组圈图
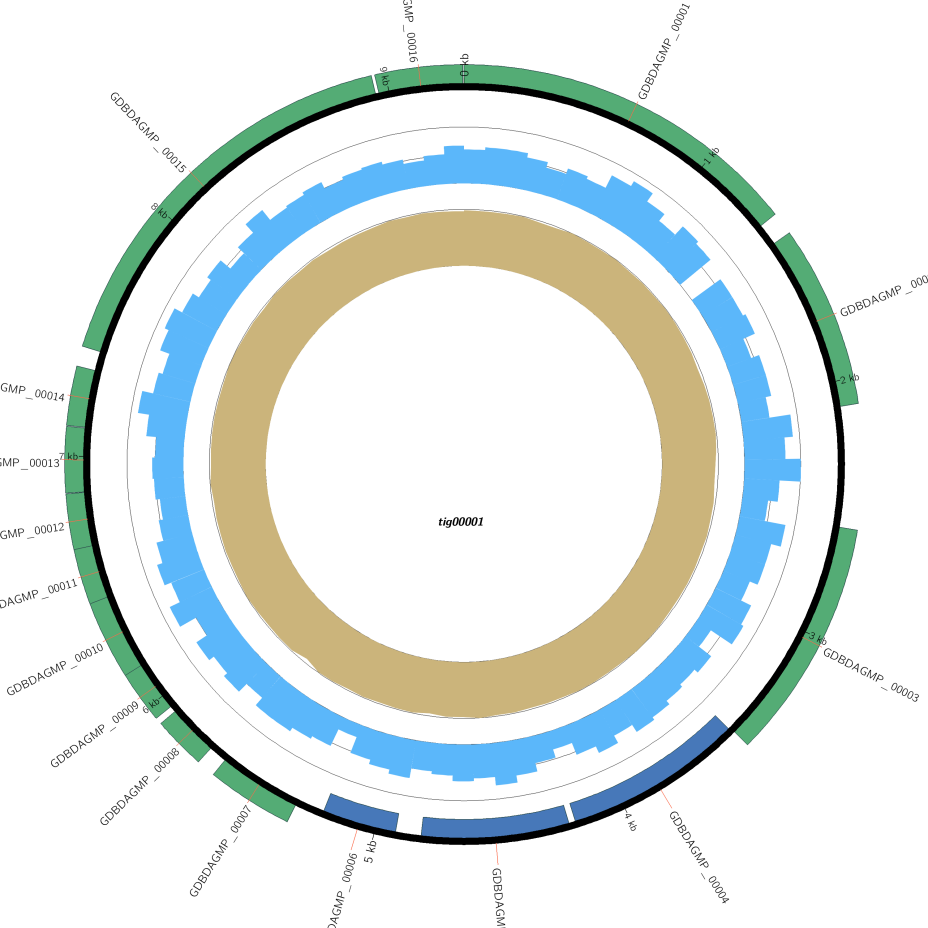 从内到外依次为深度分布,gc含量分布,编码基因(正义链)、编码基因(负义链)
从内到外依次为深度分布,gc含量分布,编码基因(正义链)、编码基因(负义链)
案例解析
案例分析一
案例解析
基于PacBio构建莲藕叶绿体基因组完成图
研究背景
莲藕作为一种白垩纪晚期遗留下来的古老双子叶植物,其叶绿体基因组序列信息的获得对于揭示双子叶植物进化以及质体形成过程有着重要的意义。
研究方法
来自武汉大学、武汉未来组的研究人员利用PacBio RS II平台得到了高质量的莲藕叶绿体基因组完成图图谱,一共产出105X的PacBio数据用于完成图组装,并使用7X、12X的Sanger、Illumina Miseq组装结果对PacBio组装结果与组装复杂度进行评估。
研究结果
1.基因组组装结果:
PacBio部分:组装得到一个163 .6Kb的完整环状基因组序列图谱,经PCR验证,组装完整度为100%。
Illumina+PCR补洞:组装得到163.7Kb的叶绿体基因组,存在两个gap区域,PCR验证发现有152bp的反向重复片段插入错误,可能是由Illumina平台的短读长引起。
Sanger+PCR补洞:组装得到163.3Kb的叶绿体基因组,PCR验证发现在ndhA区域存在282bp缺失错误,可能与Sanger测序平台的低通量有关。
2.基因组特征分析:
比对了莲藕与其他8种双子叶植物叶绿体基因组上的起始密码子使用情况。
莲藕叶绿体基因中包含了很完整的叶绿体基因集,有些叶绿体基因在被子植物进化过程中会被丢失,如与光合作用相关的ndh基因;有些基因会在进化的过程中由叶绿体基因组转移到核基因组中,比如infA。
3.系统进化分析:
通过比对莲藕与其他56种种子植物中79种叶绿体蛋白序列,利用ML法构建了系统进化树,结果表明,莲藕与一种大型陆地灌木属植物悬铃木为姐妹分支;莲属与泡花树属在进化树中为姐妹分支,印证了莲属为一种古老双子叶植物的观点;莲属分化于大约1.7亿年前,该属仅有的两个物种美洲莲和中国莲大约出现于两百万年前。
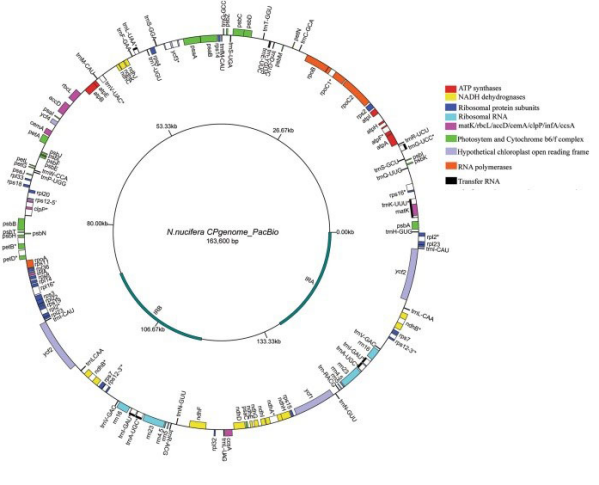
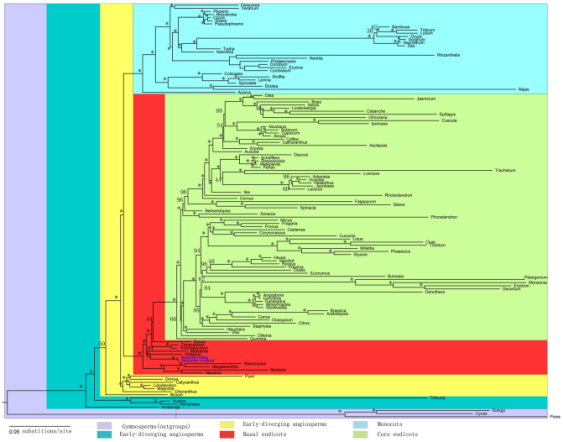
莲藕叶绿体基因组圈图 莲藕进化分析
参考文献
Wu. Z. H. et al. (2014) A precise chloroplast genome of Nelumbo nucifera (Nelumbonaceae) evaluated with Sanger, I llumina MiSeq, and PacBio RS I I sequencing platforms: insight into the plastid evolution of basal eudicots. BMC Plant Biology.



