方案策略
| 测序平台 | 测序策略 | 承诺指标 | 交付周期 |
| PacBio Sequel | 对环境样本基因组DNA进行16S/18S/ITS/功能基因全长扩增,构建文库。 | 获取全长16S序列, 每个样本6000个CCS reads。 | 建库测序:30个工作日 标准分析:5个工作日 高级分析:10个工作日 个性化分析:根据实际的信息分析内容而定 |
分析内容
标准分析
- OTU聚类分析
- 物种分类鉴定
- alpha多样性分析
- 群落组成分析
- Beta多样性分析
高级分析
- 系统进化分析
- 基于进化距离的差异分析
- 网络关联分析
结果展示
物种注释
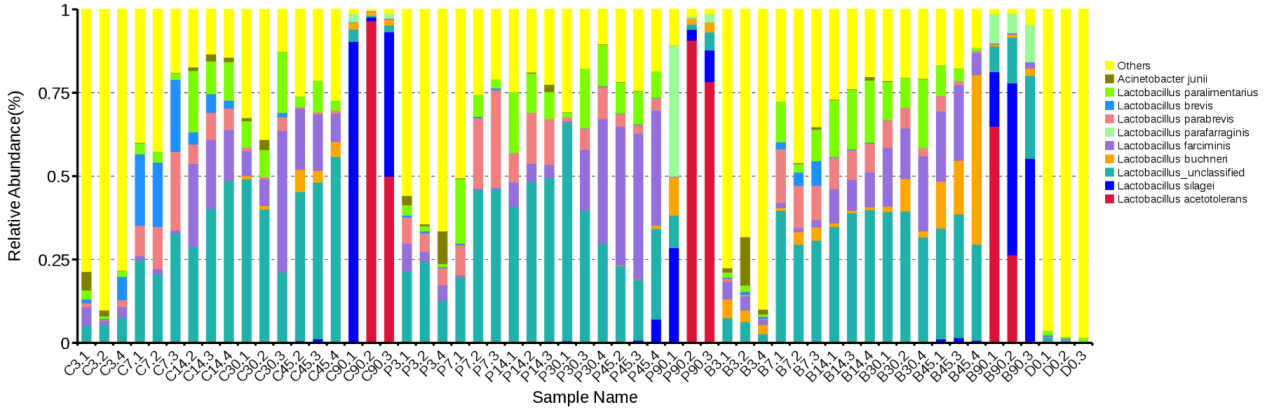 基于种水平的相对丰度柱状图
基于种水平的相对丰度柱状图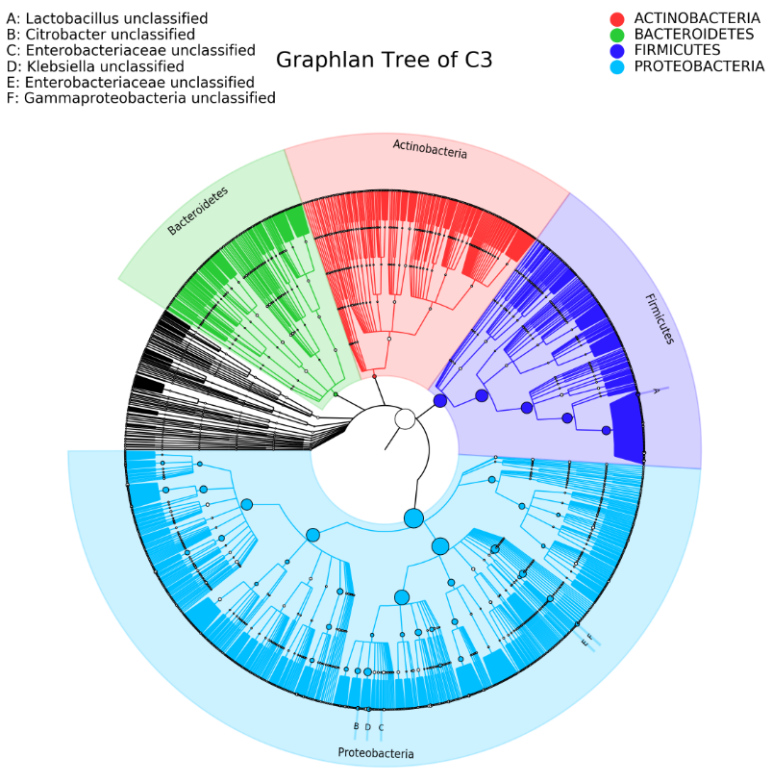 以C3组为例的Graphlan物种树
以C3组为例的Graphlan物种树Alpha多样性分析
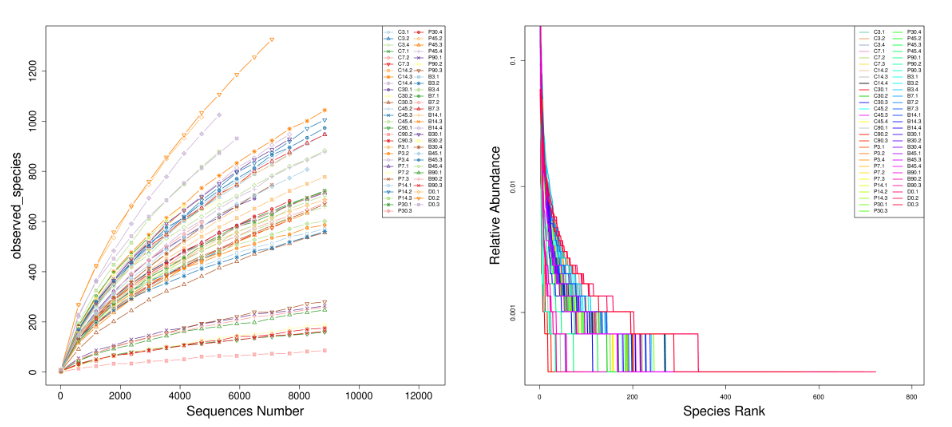 各样本alpha多样性曲线图 (左:Rarefaction Curve;右:Rank Abundance Curve)
各样本alpha多样性曲线图 (左:Rarefaction Curve;右:Rank Abundance Curve)Beta多样性分析
Beta多样性分析可以对不同样本间的群落组成结构进行分析。
 Beta多样性指数距离矩阵热度图
Beta多样性指数距离矩阵热度图高级分析
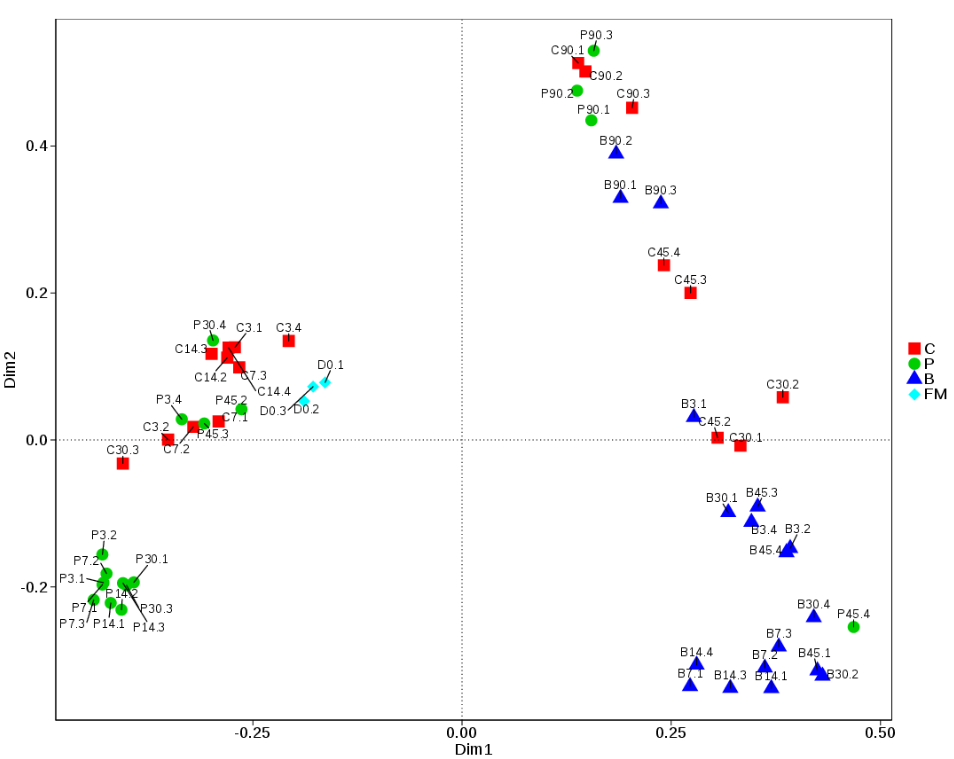 基于随机森林预测的样本相似度绘制的MDS散点图
基于随机森林预测的样本相似度绘制的MDS散点图常见问题
1. 三代扩增子测序有哪些优势?
基于PacBio SMRT单分子测序技术的超长读长优势,可覆盖全长核糖体小亚基16S/18S/ITS,解决了短读长的产品只能针对局部可变区进行分析的技术难题,在合理成本的基础上,实现真正精确的菌群分类鉴定。
案例解析
案例分析
案例解析
奶粉生产过程中细菌群落结构研究
微生物及其毒素是影响奶粉安全的重要因素,被污染的奶粉不但降低了其营养价值,而且很容易引起食用者感染细菌甚至中毒等严重后果。奶粉的微生物指标能够直接反映生产过程中的污染情况,常见的微生物主要以细菌为主。该研究采用PacBio RSII的高通量测序技术,从种的水平上研究奶粉不同生产时期细菌群落组成及变化,为微生物品质控制提供参考数据及科学有效的方法。
该研究分别采集室内小规模环境奶粉生产的6个不同时期:原始牛奶、巴氏消毒前、巴氏消毒后、第一次浓缩后、第二次浓缩后、喷雾干燥后的样品(A1-A6,B1-B6共12个样品),以及大规模工厂环境奶粉生产的3个不同时期:原始牛奶、处理前、喷雾干燥后的样品(C1-C3,D1-D3共6个样品),采用PacBio进行16S rRNA测序,比较不同时期的群落组成特征。
研究发现室内小规模环境不同生产时期的奶粉样品中细菌群落组成几乎没变化。两种优势菌Bacillus cereus和Bacillus flexus,可能来源于原始牛奶,只是相对丰度有少许变化。相反,大规模工厂环境不同生产时期的奶粉样品中微生物含量有显著的变化。
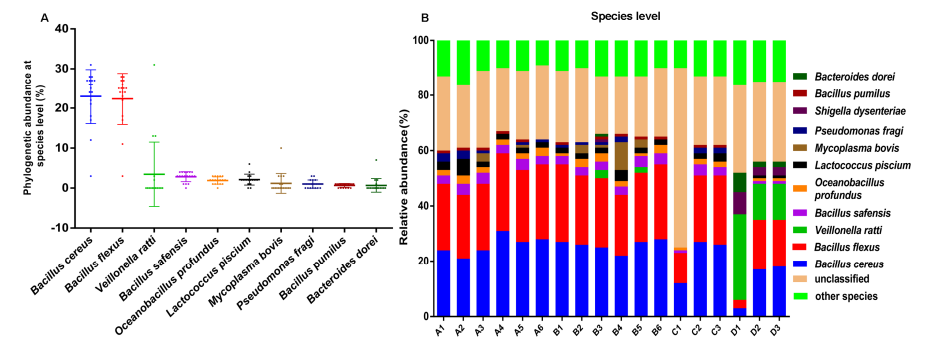 种水平细菌群落组成
种水平细菌群落组成
参考文献:
Wang J., Zheng Y., Xi X., et al. Application of PacBio Single Molecule Real-Time (SMRT) sequencing in bacterial source tracking analysis during milk powder production, Food Control (2018), doi: 10.1016/j.foodcont.2018.05.044



